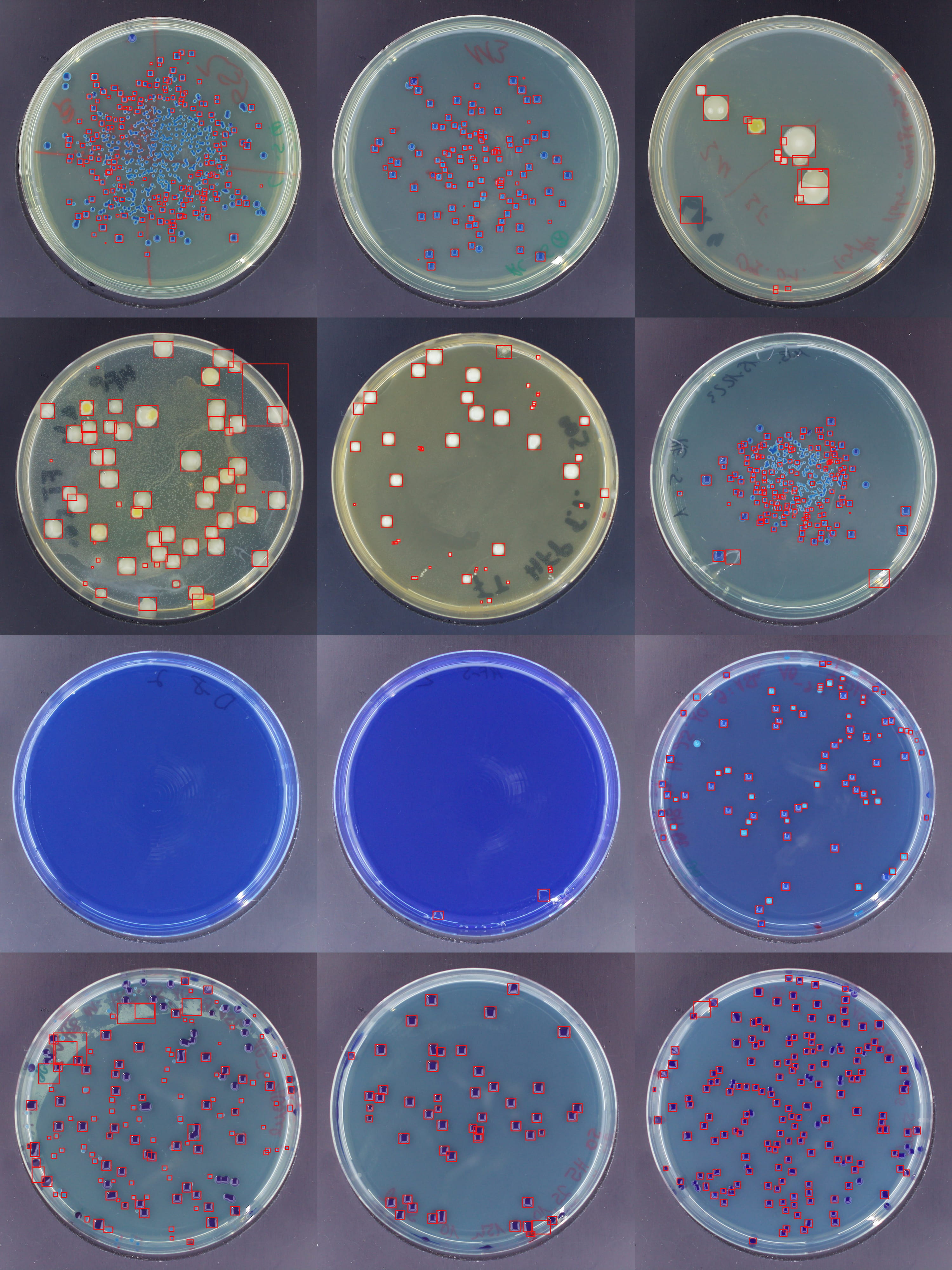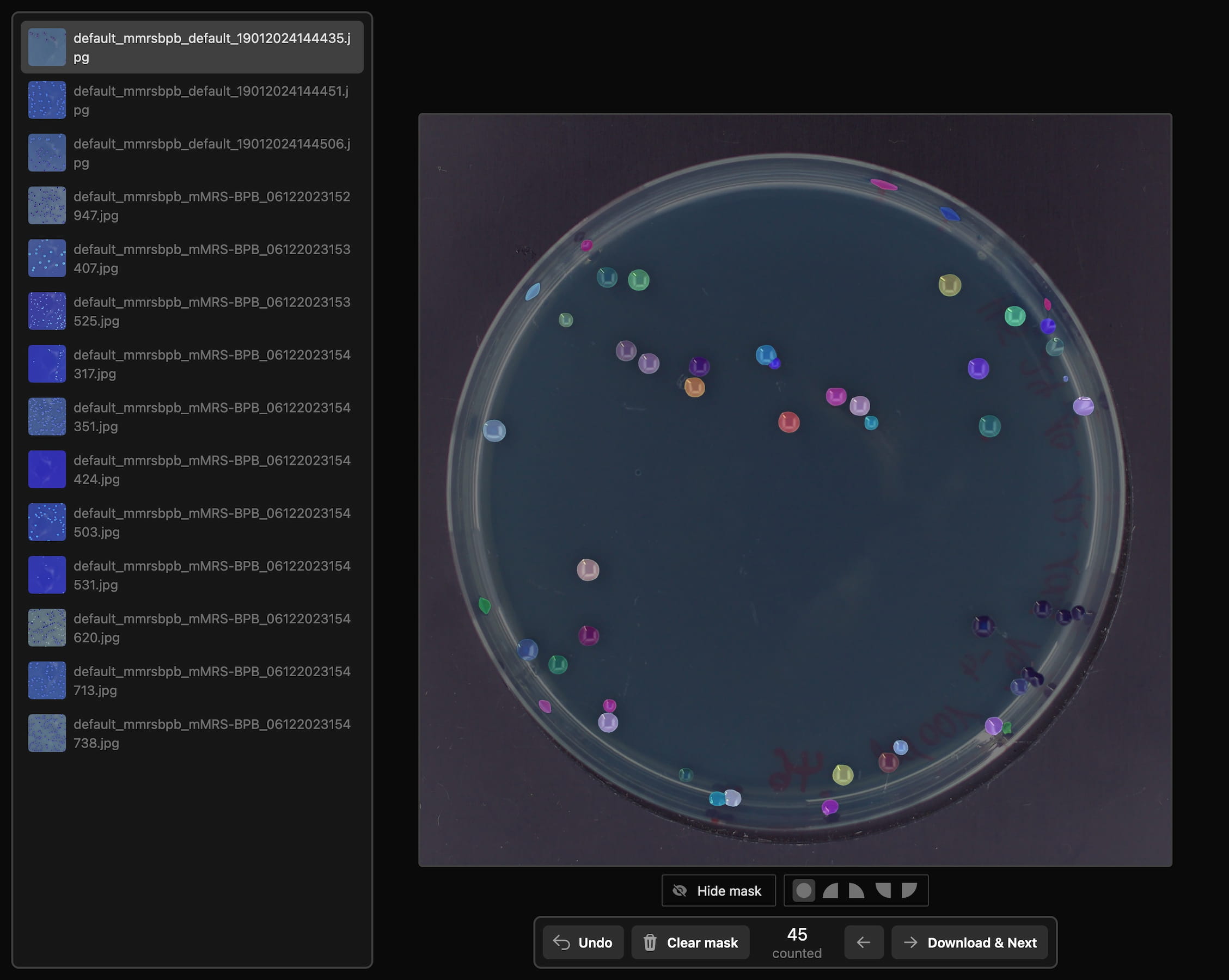
In mikrobiologischen Laboren wird das Wachstum bakterieller Kolonien nach wie vor manuell ausgezählt. Bei mehreren hundert Kolonien pro Platte und vielen Platten am Tag verschlingt das wertvolle Forschungszeit.
Die Ergebnisse hängen zudem stark von Konzentration und Erfahrung der zählenden Person ab — eine konsistente, reproduzierbare Auswertung ist auf diese Weise kaum zu erreichen.
Ich habe ein Faster-R-CNN-Modell trainiert, das Kolonien in rund vier Sekunden auf einem normalen Computer erkennt. Vorgeschaltet ist eine eigene Web-Anwendung, die Meta's Segment Anything Model (SAM) integriert — Segmentierungsmasken entstehen damit per Klick statt per Polygon-Zeichnung.
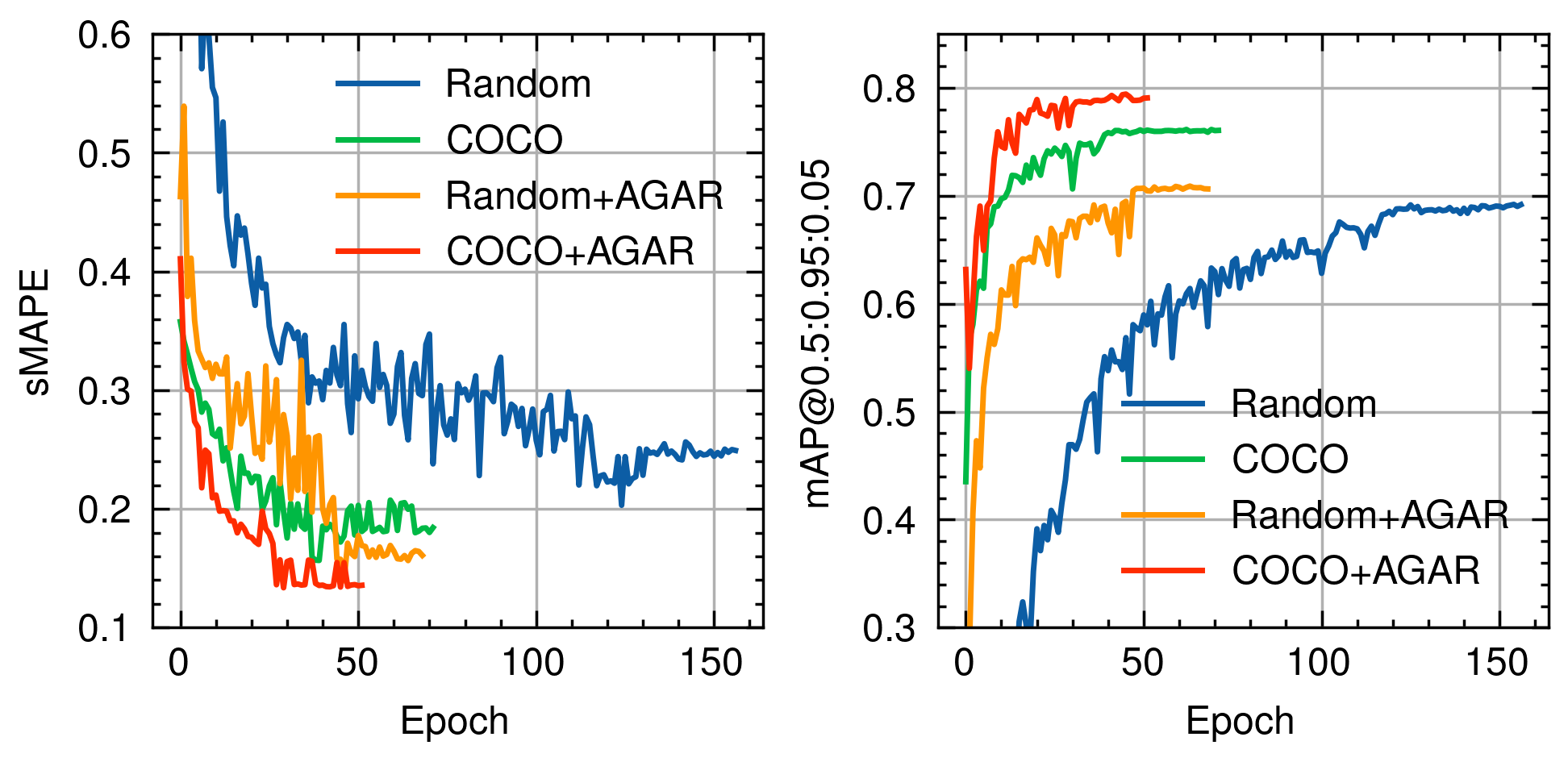
Das Modell wurde auf COCO vortrainiert, auf dem öffentlichen AGAR-Datensatz finetuned und schließlich auf 200 laboreigenen Aufnahmen einer Raspberry-Pi-Hochauflösungskamera spezialisiert. Die finale Inferenz läuft in einer Web-App, die an der FH Münster im Einsatz ist.
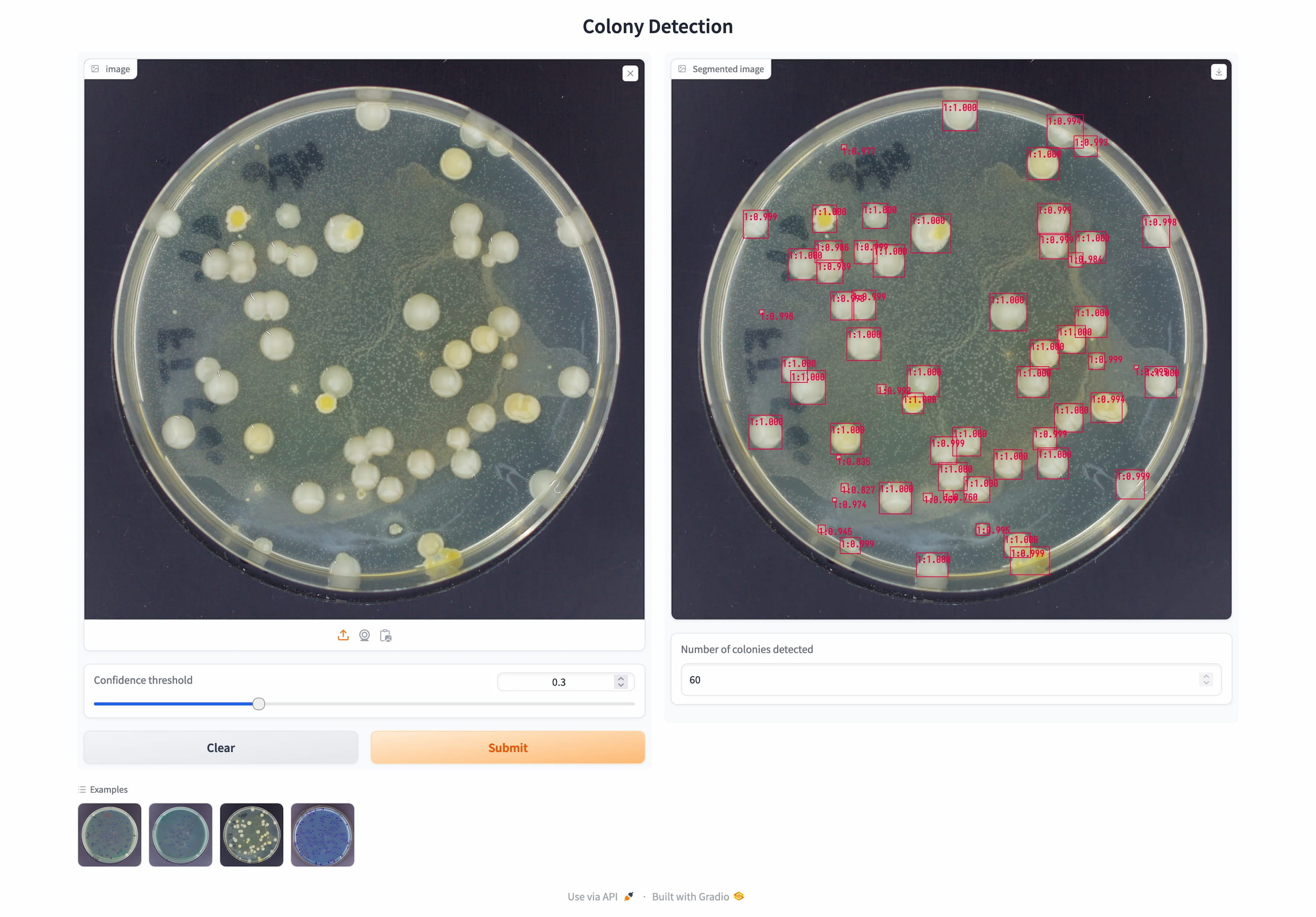
Wo manuelles Zählen mehrere Minuten pro Platte kostet, dauert die automatische Auswertung etwa vier Sekunden — bei einer Genauigkeit, die für den Laboralltag relevant ist.
Anteil korrekter Erkennungen unter allen erkannten Objekten.
Anteil tatsächlicher Kolonien, die das Modell findet.
Mittlerer absoluter Fehler in Kolonien pro Petrischale.